El objetivo de este paquete es facilitar el uso de la información que tenemos disponible en el portal de datos abiertos del gobierno sobre COVID.
Empezó como algo de uso personal que espero sirva para tomadores de decisiones, periodistas, o cualquier persona que quiera trabajar con datos sobre COVID.
Puedes instalar el paquete siguiendo estos pasos:
install.packages("devtools")
devtools::install_github("jincio/covidPeru")
Primero tenemos que llamar los data frames y luego podemos proceder con la limpieza y generar unos gráficos.
library(dplyr) ## Necesario!
library(readr) ## Necesario!
library(ggplot2) ## Necesario!
library(lubridate)## Necesario!
library(purrr) ## Necesario
library(MMWRweek) ## Necesario
library(data.table) ## Necesario
library(covidPeru)
library(covidPeru)
#> Loading covidPeru
Cargamos el último set disponible en el portal de datos abiertos de pruebas analizadas con resultado positivo.
positivos=da_positivos() # Crea un dataframe con la información positivos
head(positivos)
#> # A tibble: 6 x 14
#> UUID DEPARTAMENTO PROVINCIA DISTRITO METODODX EDAD SEXO FECHA_RESULTADO
#> <chr> <chr> <chr> <chr> <chr> <dbl> <chr> <dbl>
#> 1 7320… LIMA LIMA SAN BOR… PCR 34 FEME… 20200325
#> 2 e816… LIMA LIMA SAN BOR… PCR 30 FEME… 20200406
#> 3 71ec… LIMA LIMA SAN BOR… PCR 34 FEME… 20200410
#> 4 566a… LIMA LIMA BREÑA PCR 32 FEME… 20200403
#> 5 0275… LIMA LIMA LIMA PCR 31 FEME… 20200409
#> 6 f016… LIMA LIMA LIMA PCR 30 FEME… 20200409
#> # … with 6 more variables: year <chr>, month <chr>, day <chr>, fecha <date>,
#> # EDAD_n <dbl>, semana <dbl>
Cargamos el último set disponible en el portal de datos abiertos de fallecidos por COVID-19.
fallecidos=da_fallecidos() # Crea un dataframe con la información de fallecidos.
head(fallecidos)
#> # A tibble: 6 x 13
#> UUID FECHA_FALLECIMI… EDAD_DECLARADA SEXO FECHA_NAC DEPARTAMENTO PROVINCIA
#> <chr> <dbl> <dbl> <chr> <dbl> <chr> <chr>
#> 1 6b9e… 20200701 63 MASC… 19561228 LIMA LIMA
#> 2 beca… 20200701 63 MASC… 19570629 LIMA LIMA
#> 3 e5c2… 20200701 67 MASC… 19530524 LA LIBERTAD ASCOPE
#> 4 e844… 20200701 59 MASC… 19610210 LA LIBERTAD TRUJILLO
#> 5 dfe8… 20200701 61 FEME… 19581113 LA LIBERTAD TRUJILLO
#> 6 d780… 20200701 54 FEME… 19650921 LA LIBERTAD VIRU
#> # … with 6 more variables: DISTRITO <chr>, year <chr>, month <chr>, day <chr>,
#> # fecha <date>, semana <dbl>
Cargamos el último set de SINADEF disponible en el portal de datos abiertos. Este demora un poco más, tengan paciencia!.
sinadef=da_sinadef()
head(sinadef)
#> # A tibble: 6 x 6
#> fecha semana year dia `DEPARTAMENTO DOMICILI… `PROVINCIA DOMICILI…
#> <date> <dbl> <dbl> <chr> <chr> <chr>
#> 1 2020-01-22 4 2020 Wednesday LIMA LIMA
#> 2 2020-01-24 4 2020 Friday CUSCO CUSCO
#> 3 2020-01-30 5 2020 Thursday CALLAO CALLAO
#> 4 2020-01-19 4 2020 Sunday CAJAMARCA CAJAMARCA
#> 5 2020-01-13 3 2020 Monday LA LIBERTAD TRUJILLO
#> 6 2020-01-25 4 2020 Saturday CAJAMARCA CAJAMARCA
Una vez con las bases podemos usar las otras funciones para generar series diarias y algunos gráficos de estas series.
Las funcion entrega una lista con dos objetos: una data y un gráfico.
fdiarios=fallecidos_diarios(fallecidos)[[1]]
head(fdiarios)
#> # A tibble: 6 x 2
#> fecha count
#> <date> <int>
#> 1 2020-03-18 1
#> 2 2020-03-19 3
#> 3 2020-03-20 2
#> 4 2020-03-21 1
#> 5 2020-03-22 2
#> 6 2020-03-23 1
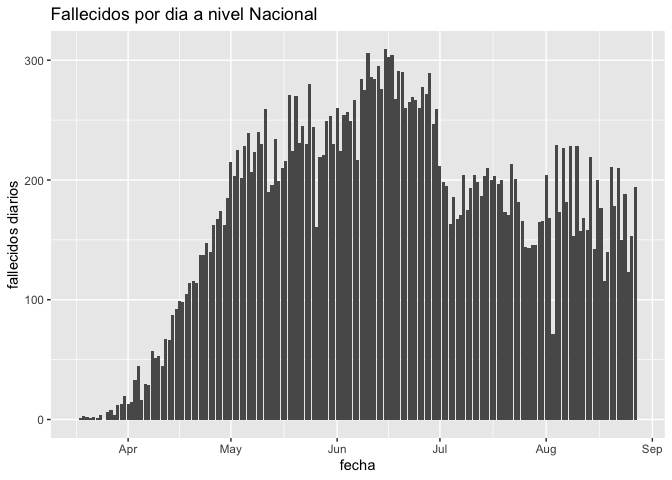
grafico=fallecidos_diarios(fallecidos)[[2]]
print(grafico)
Podemos identificar un departamento en específico.
fdiarios=fallecidos_diarios(fallecidos, "lima")[[1]]
head(fdiarios)
#> # A tibble: 6 x 3
#> # Groups: DEPARTAMENTO [1]
#> DEPARTAMENTO fecha count
#> <chr> <date> <int>
#> 1 LIMA 2020-03-18 1
#> 2 LIMA 2020-03-19 3
#> 3 LIMA 2020-03-20 2
#> 4 LIMA 2020-03-23 1
#> 5 LIMA 2020-03-24 2
#> 6 LIMA 2020-03-26 3
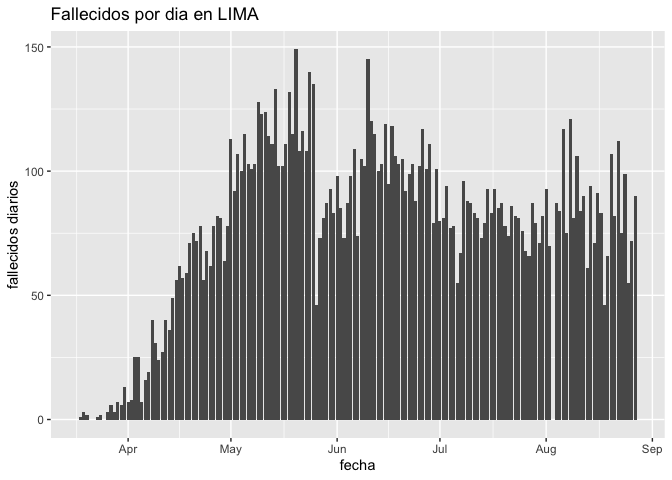
grafico=fallecidos_diarios(fallecidos, "lima")[[2]]
print(grafico)
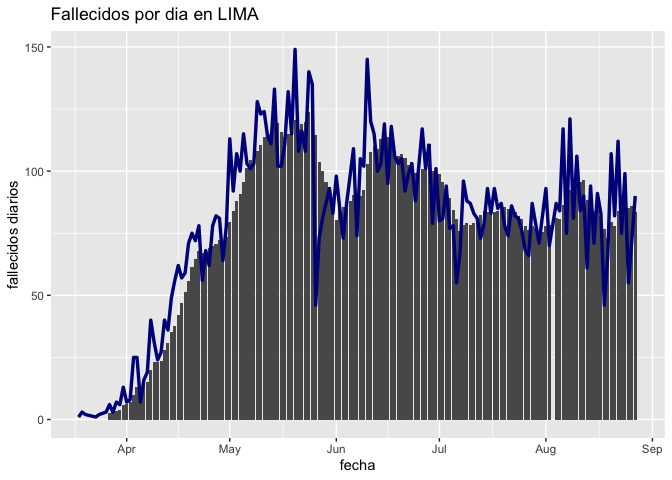
- Podemos agregar una media móvil también.
grafico=fallecidos_diarios(fallecidos, "lima",mediamovil = 7)[[2]]
print(grafico)
#> Warning: Removed 6 rows containing missing values (position_stack).
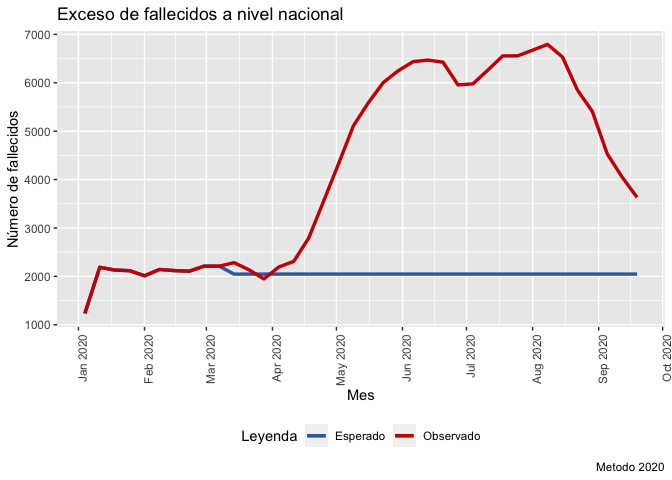
En el paquete también está disponible la función para calcular el exceso de muertos en Perú y por departamentos por semana.
En este caso la información se calcula por semana. Hay dos “métodos” disponibles. El método por default toma como referencia las primeras 11 semanas del 2020 (“M2020”), y el “alternativo” que usa el promedio de muertos de los años 2017,2018, 2019 con la semana de comparación.
base=exceso_muertes(sinadef)[1]
#> [1] "Ojo: archivo actualizado al 2020-09-23 tomamos referencia hasta la semana 38"
head(base,30)
#> [[1]]
#> # A tibble: 38 x 6
#> semana year numero_fallecidos Esperado Exceso fecha_ultima
#> <dbl> <dbl> <int> <dbl> <dbl> <date>
#> 1 1 2020 1233 1233 0 2020-01-04
#> 2 2 2020 2187 2187 0 2020-01-11
#> 3 3 2020 2130 2130 0 2020-01-18
#> 4 4 2020 2117 2117 0 2020-01-25
#> 5 5 2020 2011 2011 0 2020-02-01
#> 6 6 2020 2142 2142 0 2020-02-08
#> 7 7 2020 2119 2119 0 2020-02-15
#> 8 8 2020 2107 2107 0 2020-02-22
#> 9 9 2020 2211 2211 0 2020-02-29
#> 10 10 2020 2210 2210 0 2020-03-07
#> # … with 28 more rows
grafico=exceso_muertes(sinadef)[2]
#> [1] "Ojo: archivo actualizado al 2020-09-23 tomamos referencia hasta la semana 38"
print(grafico)
#> [[1]]
grafico=exceso_muertes(sinadef,metodo = FALSE)[2]
#> [1] "Ojo: archivo actualizado al 2020-09-23 tomamos referencia hasta la semana 38"
print(grafico)
#> [[1]]
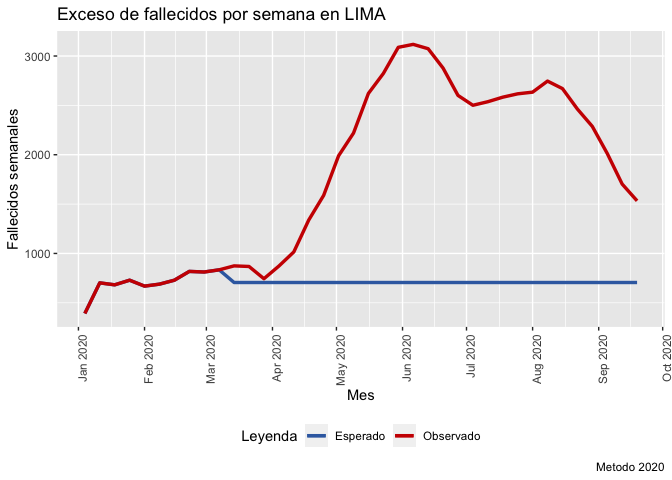
Lima
Lima=exceso_muertes(sinadef,"Lima")[2]
#> [1] "Ojo: archivo actualizado al 2020-09-23 tomamos referencia hasta la semana 38"
print(Lima)
#> [[1]]
** Gabriel Carrasco-Escobar (Gabc91) preparó una función que hemos agregado al paquete. La función te da como resultado un gráfico a modo de panel de calor con el exceso de muertes para todas las regiones **
grafico=panel_exceso(sinadef)
print(grafico)
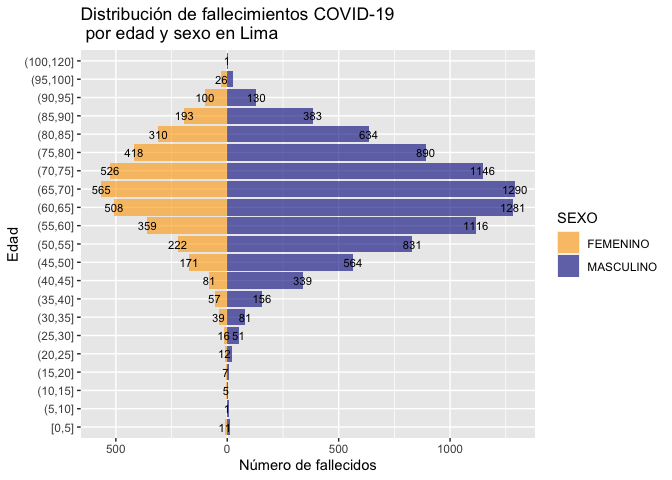
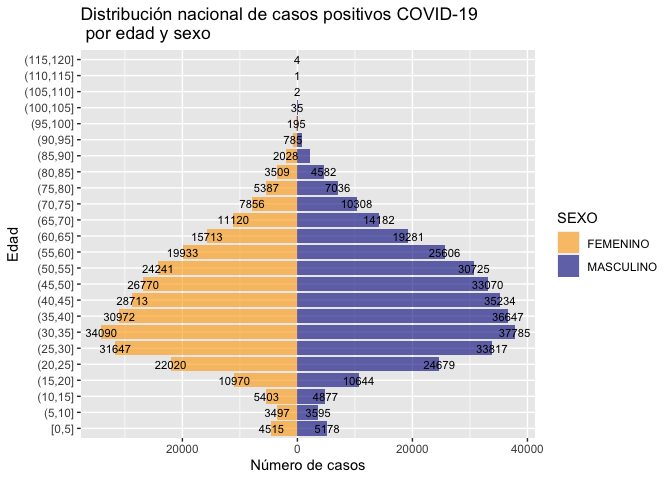
** Juan Gamboa Unsihuay (jesuseduardog) preparó una función que hemos agregado al paquete. La función te da como resultado una base y un gráfico que describen la población contagiada y la población fallecida por sexo y edad. El gráfico tiene una forma piramidal y su eficacia reside en que permite caracterizar la distribución por edad y sexo de un colectivo determinado, en este caso el grupo de casos covid positivos y el grupo de fallecidos covid. Esto a nivel nacional como a nivel departamental.
Lima
base = piramide_fcovid(fallecidos,"Lima")[[1]]
head(base)
#> # A tibble: 6 x 3
#> # Groups: SEXO, EDAD_CAT [6]
#> SEXO EDAD_CAT n
#> <chr> <fct> <int>
#> 1 FEMENINO [0,5] 11
#> 2 FEMENINO (5,10] 1
#> 3 FEMENINO (10,15] 5
#> 4 FEMENINO (15,20] 7
#> 5 FEMENINO (20,25] 12
#> 6 FEMENINO (25,30] 16
grafico = piramide_fcovid(fallecidos,"Lima")[[2]]
print(grafico)
Nacional
base <- piramide_pcovid(positivos)[[1]]
head(base)
#> # A tibble: 6 x 3
#> # Groups: SEXO, EDAD_CAT [6]
#> SEXO EDAD_CAT n
#> <chr> <fct> <int>
#> 1 FEMENINO [0,5] 4515
#> 2 FEMENINO (5,10] 3497
#> 3 FEMENINO (10,15] 5403
#> 4 FEMENINO (15,20] 10970
#> 5 FEMENINO (20,25] 22020
#> 6 FEMENINO (25,30] 31647
grafico = piramide_pcovid(positivos)[[2]]
print(grafico)
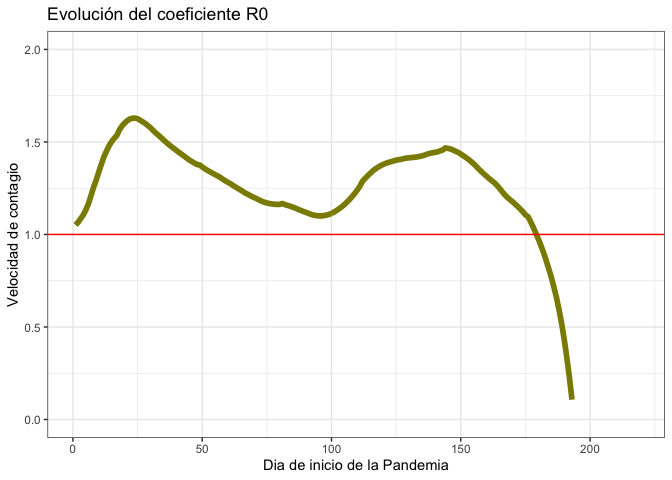
** Cesar Urquizo (CUrquizoU) preparo una función que hemos agregado al paquete. Esta funcion replica el modelo del documento de investigación Estimating and simulating a SIRD Model of COVID-19 for many countries, states, and cities de Jesus Fernandez Villaverde y Charles Jones (2020).
El modelo permite reconstruir a partir de la base de fallecidos del SINADEF, los casos de fallecidos, casos positivos, población vulnerable y población recuperada. Asimismo, se calcula la velocidad de contagio del virus o también denominado R0. Lo importante de este modelo es que permite conocer la dinamica de las principales variables como la evolución de los casos de fallecidos, contagiados o recuperados.
Resultados de la estimación
resultados <- sird_villaverde(sinadef,"Lima")
Población suceptible
S <- resultados[["S"]]
head(S)
#> [1] 11245182 11241647 11238049 11234361 11230574 11226654
R0
r0 <- resultados[["R0"]]
head(r0)
#> [1] 1.051583 1.065327 1.085292 1.105263 1.132675 1.165557
Adicional, el paquete contiene la función sird_graficos que permite realizar una inspección gráfica de los resultados obtenidos del modelo Villaverde.
Principales variables SIRD
graficos <- sird_graficos(resultados)
R0
print(graficos[[1]])
print(graficos[[2]])
#> Warning: Removed 25 row(s) containing missing values (geom_path).