Supervised Learning Practices Using ‘tidymodels’
livedoorニュースコーパスを用いた文書分類について、日本語テキストの分かち書きに使うトークナイザを差し替えながら試しています。
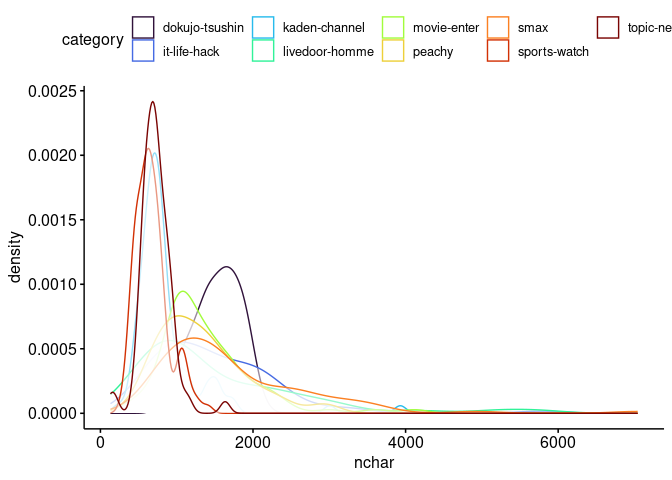
コーパスのカテゴリごとの平均的な分量は次のようになっています。
suppressPackageStartupMessages({
require(targets)
require(tidymodels)
require(textrecipes)
})
tidymodels::tidymodels_prefer(quiet = TRUE)
tar_read(nchar_summary)
#> # A tibble: 9 × 7
#> category nchar_mean nchar_median nchar_min nchar_max nchar_total n
#> <fct> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl>
#> 1 dokujo-tsushin 1529 1559 870 2122 117757 77
#> 2 it-life-hack 1493 1326 328 5773 120964 81
#> 3 kaden-channel 864 747 229 3931 77764 90
#> 4 livedoor-homme 1534 1121 393 5731 84393 55
#> 5 movie-enter 1383 1227 312 4118 116239 84
#> 6 peachy 1325 1223 392 2992 110057 83
#> 7 smax 1741 1432 599 7042 151471 87
#> 8 sports-watch 674 641 292 1411 74206 110
#> 9 topic-news 722 706 132 1635 50606 70
tar_read(nchar_density)次のRパッケージによる分かち書きを試しています。
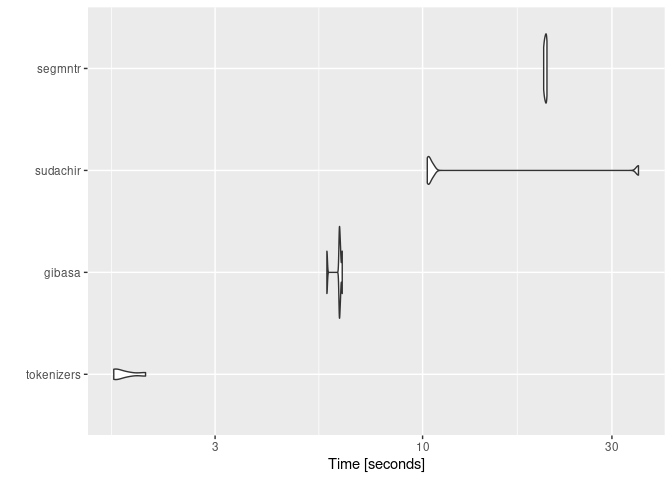
ここでは文字列の正規化などはおこなわず、コーパスの本文を直接分かち書きしています。gibasaについては付与された品詞にもとづいて語彙をフィルタしています。
segmntrは、点予測にもとづく形態素解析器であるVaporetteのラッパーです。VaporetteのバイナリはMeCabよりも高速ですが、segmntrでは関数を呼ぶたびにモデルファイルを読みこむ時間を要するため、ここではgibasa(MeCabをマルチスレッドで呼んでいる)のほうが解析速度が速くなっています。
source("R/rec.R")
dummy_data <-
tibble::tibble(
doc_id = seq_along(ldccr::NekoText),
body = ldccr::NekoText,
category = sample.int(9, length(ldccr::NekoText), replace = TRUE)
) |>
dplyr::filter(nchar(body) > 50)
bench <-
microbenchmark::microbenchmark(
tokenizers = default_rec(dummy_data) |>
recipes::prep() |>
recipes::bake(new_data = NULL),
gibasa = gibasa_rec(dummy_data) |>
recipes::prep() |>
recipes::bake(new_data = NULL),
sudachir = sudachir_rec(dummy_data) |>
recipes::prep() |>
recipes::bake(new_data = NULL),
segmntr = segmntr_rec(dummy_data) |>
recipes::prep() |>
recipes::bake(new_data = NULL),
times = 5,
check = NULL
)
#> as(<dgTMatrix>, "dgCMatrix") is deprecated since Matrix 1.5-0; do as(., "CsparseMatrix") instead
bench
#> Unit: seconds
#> expr min lq mean median uq max neval
#> tokenizers 1.666544 1.675393 1.770761 1.696340 1.811516 2.004011 5
#> gibasa 5.739378 6.169449 6.113071 6.174713 6.208225 6.273589 5
#> sudachir 10.276305 10.337284 15.326154 10.393506 10.631952 34.991725 5
#> segmntr 20.189705 20.309172 20.397947 20.406017 20.506926 20.577916 5
#> cld
#> a
#> ab
#> bc
#> c
ggplot2::autoplot(bench)
#> Coordinate system already present. Adding new coordinate system, which will
#> replace the existing one.tidymodelsを用いてXGBoostのモデルを学習しています。わずかな差ですが、segmntrを用いたときが精度のよいモデルを学習できています。
tar_read(best_models)
#> # A tibble: 5 × 9
#> wflow_id .config .metric mean std_err n prepr…¹ model rank
#> <chr> <chr> <chr> <dbl> <dbl> <int> <chr> <chr> <int>
#> 1 segmntr_boost_tree Prepro… f_meas 0.812 0.0305 3 recipe boos… 1
#> 2 gibasa_boost_tree Prepro… f_meas 0.808 0.0191 3 recipe boos… 2
#> 3 sudachir_boost_tree Prepro… f_meas 0.792 0.0111 3 recipe boos… 3
#> 4 gibasa_with_filter_bo… Prepro… f_meas 0.784 0.00557 3 recipe boos… 4
#> 5 default_boost_tree Prepro… f_meas 0.758 0.0213 3 recipe boos… 5
#> # … with abbreviated variable name ¹preprocessorここで最終的に作成されるモデルは次のようになります。
(wflow <- tar_read(corp_wflow))
#> ══ Workflow ════════════════════════════════════════════════════════════════════
#> Preprocessor: Recipe
#> Model: boost_tree()
#>
#> ── Preprocessor ────────────────────────────────────────────────────────────────
#> 3 Recipe Steps
#>
#> • step_tokenize()
#> • step_tokenfilter()
#> • step_texthash()
#>
#> ── Model ───────────────────────────────────────────────────────────────────────
#> Boosted Tree Model Specification (classification)
#>
#> Main Arguments:
#> trees = 300
#> tree_depth = 1
#> learn_rate = 0.2
#> loss_reduction = 0.00626153110866815
#> sample_size = 0.837367888679728
#> stop_iter = 5
#>
#> Engine-Specific Arguments:
#> nthread = max(1, parallel::detectCores(logical = FALSE) - 1, na.rm = 1)
#>
#> Computational engine: xgboost
(corpus <- tar_read(corp_split))
#> <Training/Testing/Total>
#> <549/188/737>
ret <- tune::last_fit(wflow, corpus)ret |>
tune::collect_predictions() |>
yardstick::f_meas(truth = category, estimate = .pred_class)
#> # A tibble: 1 × 3
#> .metric .estimator .estimate
#> <chr> <chr> <dbl>
#> 1 f_meas macro 0.841